Aislamiento y caracterización filogenética de bacterias nativas cultivables proce-dentes de minas abandonadas en Tacna, Perú.
DOI:
https://doi.org/10.18633/biotecnia.v26.2130Palabras clave:
Bacteria nativa, Minas abandonadas, Contaminación de suelos, Reconstrucción filogenética, BiorremediaciónResumen
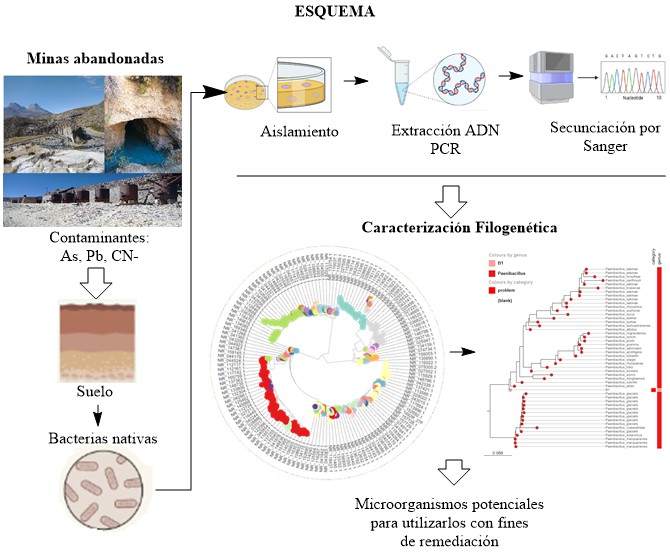
Las bacterias nativas adaptadas a ambientes contaminadas han demostrado su gran capacidad de sobrevivir en condiciones adversas. El objetivo de este estudio fue identificar las bacterias presentes en suelos de minas abandonadas, además de investigar las relaciones filogenéticas de estas bacterias nativas cultivables. Se realizó el aislamiento bacteriano, la extracción de ADN, amplificación por PCR, secuenciación del gen 16S ARNr, reconstrucción filogenética de Máxima Verosimilitud (ML) con RaXML, e identificación de géneros relacionadas con microreact. Las secuencias obtenidas fueron editadas a un tamaño de 1200 – 1400 pb, que posteriormente se compararon con 1137 secuencias procedentes de la base de datos del GenBank. Los nueve aislamientos obtenidos se agruparon filogenéticamente en seis grupos que corresponderían a los géneros Bacillus, Cytobacillus, Paenibacillus, Microbacterium, Peribacillus, Acinetobacter. Por lo tanto, se resalta el potencial inexplorado de estas bacterias para ser utilizadas en procesos de biorremediación. Además, algunas de estas bacterias pueden ser propuestos como indicadores de contaminación, lo que amerita realizar una investigación más detallada debido a que estos microorganismos pueden ser empleados en futuras investigaciones.
Descargas
Citas
Abdel-Razek, A. S., Refaat, B. M., Abdel-Shakour, E. H., Zaher, R., Mohamed, M. K. 2015. Biodegrada-tion of Phenol by Microbacterium terregenes Isolated from oil field NORM SOIL. Journal of Applied & Environmental Microbiology. 3(3):63–69. Disponible en: https://citeseerx.ist.psu.edu/document?repid=rep1&type=pdf&doi=abdea133f179c569675289bdbc82d9431ad28f51
Agarry, S. A., Owabor, C. N., Yusuf, R. O. 2010. Bioremediation of soil artificially contaminated with petroleum hydrocarbon oil mixtures: Evaluation of the use of animal manure and chemical fertilizer. Bioremediation Journal. 14(4):189–195. https://doi.org/10.1080/10889868.2010.514965
Agboola, O., Babatunde, D. E., Isaac Fayomi, O. S., Sadiku, E. R., Popoola, P., Moropeng, L., Yahaya, A., Mamudu, O. A. 2020. A review on the impact of mining operation: Monitoring, assessment and man-agement. Results in Engineering. 8:1–23. https://doi.org/10.1016/j.rineng.2020.100181
Ali, H., Khan, E. 2017. What are heavy metals? Long-standing controversy over the scientific use of the term ‘heavy metals’–proposal of a comprehensive definition. Toxicological and Environmental Chem-istry. 1–26. https://doi.org/10.1080/02772248.2017.1413652
Alotaibi, B. S., Khan, M., Shamim, S. 2021. Unraveling the underlying heavy metal detoxification mecha-nisms of bacillus species. Microorganisms. 9(8):1–31. https://doi.org/10.3390/microorganisms9081628
Altimira, F., Yáñez, C., Bravo, G., González, M., Rojas, L. A., Seeger, M. 2012. Characterization of cop-per-resistant bacteria and bacterial communities from copper-polluted agricultural soils of central Chile. BMC Microbiology. 12(193):1–12. https://doi.org/10.1186/1471-2180-12-193
Amrane, A., Nguyen, T. A., Mohan, D., Yasin, G. y Assadi, A. A. 2020. Nanomaterials for Soil Remedia-tion. En: Micro & Nano Technologies Series. Amrane, D. Mohan, T. A. Nguyen, A. A. Assadi, y G. Yasin (eds.), pp 1-24. Elsevier. https://doi.org/10.1016/B978-0-12-822891-3.00021-9
AnalytikJena, Instructions for Use: innuPREP DNA/RNA Mini Kit. [Consultado 13 de febrero 2023] 2017. Disponible en: https://www.analytik-jena.fr/fileadmin/content/pdf_life_science/Manual/Manual_innuPREP_DNA_RNA_Mini_Kit.pdf
Aniszewski, E., Silva, R., Faria, F., Ferreira, S. G., Soares, A. 2010. Bioemulsifier production by Micro-bacterium sp. strains isolated from mangrove and their application to remove cadmiun and zinc from hazardous industrial residue. Brazilian Journal of Microbiology. 41:235–245. https://doi.org/10.1590/S1517-83822010000100033
Arce-Inga, M., González-Pérez, A. R., Hernandez-Diaz, E., Chuquibala-Checan, B., Chavez-Jalk, A., Llanos-Gomez, K. J., Leiva-Espinoza, S. T., Oliva-Cruz, S. M., Cumpa-Velasquez, L. M. 2022. Bio-remediation Potential of Native Bacillus sp. Strains as a Sustainable Strategy for Cadmium Accumula-tion of Theobroma cacao in Amazonas Region. Microorganisms. 10(11):1–19. https://doi.org/10.3390/microorganisms10112108
Ayangbenro, A. S., Babalola, O. O. 2020. Genomic analysis of Bacillus cereus NWUAB01 and its heavy metal removal from polluted soil. Scientific Reports. 10(1). https://doi.org/10.1038/s41598-020-75170-x
Bala, S., Garg, D., Thirumalesh, B. V., Sharma, M., Sridhar, K., Inbaraj, B. S., Tripathi, M. 2022. Recent Strategies for Bioremediation of Emerging Pollutants: A Review for a Green and Sustainable Envi-ronment. Toxics. 10(8):1–24. https://doi.org/10.3390/toxics10080484
Bazzi, W., Abou, A. G., Nasser, A., Haraoui, L. P., Dewachi, O., Abou-Sitta, G., Nguyen, V. K., Abara, A., Karah, N., Landecker, H., Knapp, C., McEvoy, M. M., Zaman, M. H., Higgins, P. G., Matar, G. M. 2020. Heavy Metal Toxicity in Armed Conflicts Potentiates AMR in A. baumannii by Selecting for Antibiotic and Heavy Metal Co-resistance Mechanisms. Frontiers in Microbiology. 11:1–12. https://doi.org/10.3389/fmicb.2020.00068
Bini, C., Maleci, L. y Wahsha, M. 2017. Mine Waste: Assessment of Environmental Contamination and Restoration. En: Assessment, Restoration and Reclamation of Mining Influenced Soils, pp. 89–134. Elsevier Inc. https://doi.org/10.1016/B978-0-12-809588-1.00004-9
Bôto, M., Magalhães, C., Perdigão, R., Alexandrino, D., Fernandes, J.., Bernabeu, A., Ramos, S., Carvalho, M., Semedo, M., LaRoche, J., Almeida, C., Mucha, A. 2021. Harnessing the Potential of Native Microbial Communities for Bioremediation of Oil Spills in the Iberian Peninsula NW Coast. Frontiers in Microbiology, 12(April). https://doi.org/10.3389/fmicb.2021.633659.
Cai, Y., Wang, R., Rao, P., Wu, B., Yan, L., Hu, L., Park, S., Ryu, M., Zhou, X. 2021. Bioremediation of petroleum hydrocarbons using Acinetobacter sp. SCYY-5 isolated from contaminated oil sludge: Strategy and effectiveness study. International Journal of Environmental Research and Public Health. 18(2):1–14. https://doi.org/10.3390/ijerph18020819
Candeias, C., Ávila, P., Coelho, P. y Teixeira, J. P. 2019. Mining activities: Health impacts. En: Encyclope-dia of Environmental Health. 2nd ed. Elsevier Inc. https://doi.org/10.1016/B978-0-12-409548-9.11056-5
Chandran, H., Meena, M., & Sharma, K. (2020). Microbial Biodiversity and Bioremediation Assessment Through Omics Approaches. Frontiers in Environmental Chemistry, 1(September), 1–22. https://doi.org/10.3389/fenvc.2020.570326
Clarridge, J. E. 2004. Impact of 16S rRNA gene sequence analysis for identification of bacteria on clinical microbiology and infectious diseases. Clinical Microbiology Reviews. 17(4):840–862. https://doi.org/10.1128/CMR.17.4.840-862.2004
Coelho, P., & Teixeira, J. P. (2011). Mining activities: Health impacts. In J. Nriagu (Ed.), Encyclopedia of Environmental Health (2nd ed., pp. 788–802). Elsevier B.V. https://doi.org/10.1016/B978-0-12-409548-9.11056-5
Çolak, F., Olgun, A., Atar, N., Yazicioĝlu, D. 2013. Heavy metal resistances and biosorptive behaviors of Paenibacillus polymyxa: Batch and column studies. Journal of Industrial and Engineering Chemistry. 19:863–869. https://doi.org/10.1016/j.jiec.2012.11.001
Corretto, E., Antonielli, L., Sessitsch, A., Höfer, C., Puschenreiter, M., Widhalm, S., Swarnalakshmi, K., Brader, G. 2020. Comparative Genomics of Microbacterium Species to Reveal Diversity, Potential for Secondary Metabolites and Heavy Metal Resistance. Frontiers in Microbiology. 11:1–17. https://doi.org/10.3389/fmicb.2020.01869
Corretto, E., Antonielli, L., Sessitsch, A., Kidd, P., Weyens, N., Brader, G. 2015. Draft genome sequences of 10 Microbacterium spp., with emphasis on heavy metalcontaminated environments. Genome An-nouncements. 3(3):1–3. https://doi.org/10.1128/genomeA.00432-15
Dawwam, G. E., Abdelfattah, N. M., Abdel-Monem, M. O., Jahin, H. S., Omer, A. M., Abou-Taleb, K. A., Mansor, E. S. 2023. An immobilized biosorbent from Paenibacillus dendritiformis dead cells and polyethersulfone for the sustainable bioremediation of lead from wastewater. Scientific Reports. 13(1):1–16. https://doi.org/10.1038/s41598-023-27796-w
Dhakephalkar, P. K., Chopade, B. A. 1994. High levels of multiple metal resistance and its correlation to antibiotic resistance in environmental isolates of Acinetobacter. BioMetals. 7(1):67–74. https://doi.org/10.1007/BF00205197
Dos Santos, H. R. M., Argolo, C. S., Argôlo-Filho, R. C., & Loguercio, L. L. 2019. A 16S rDNA PCR-based theoretical to actual delta approach on culturable mock communities revealed severe losses of diversity information, BMC Microbiology, 19(1), pp. 1–14. doi: 10.1186/s12866-019-1446-2.
Fernandes, C. C., Kishi, L. T., Lopes, E. M., Omori, W. P., Souza, J. A. M. de, Alves, L. M. C., Lemos, E. G. de M. 2018. Bacterial communities in mining soils and surrounding areas under regeneration pro-cess in a former ore mine. Brazilian Journal of Microbiology. 49(3):1–14. https://doi.org/10.1016/j.bjm.2017.12.006
Grady, E. N., MacDonald, J., Liu, L., Richman, A., Yuan, Z. C. 2016. Current knowledge and perspectives of Paenibacillus: A review. Microbial Cell Factories. 15(203):1–18. https://doi.org/10.1186/s12934-016-0603-7
Guo, H., Luo, S., Chen, L., Xiao, X., Xi, Q., Wei, W., Zeng, G., Liu, C., Wan, Y., Chen, J., He, Y. 2010. Bioremediation of heavy metals by growing hyperaccumulaor endophytic bacterium Bacillus sp. L14. Bioresource Technology. 101:8599–8605. https://doi.org/10.1016/j.biortech.2010.06.085
Gupta, N., Balomajumder, C., Agarwal, V. K. 2010. Enzymatic mechanism and biochemistry for cyanide degradation : A review. Journal of Hazardous Materials. 176:1–13. https://doi.org/10.1016/j.jhazmat.2009.11.038
Hassler, H. B., Probert, B., Moore, C., Lawson, E., Jackson, R. W., Russell, B. T., Richards, V. P. 2022. Phylogenies of the 16S rRNA gene and its hypervariable regions lack concordance with core genome phylogenies. Microbiome. 10(1):1–18. https://doi.org/10.1186/s40168-022-01295-y
Ho, M. T., Li, M. S. M., McDowell, T., MacDonald, J., Yuan, Z. C. 2020. Characterization and genomic analysis of a diesel-degrading bacterium, Acinetobacter calcoaceticus CA16, isolated from Canadian soil. BMC Biotechnology. 20(39):1–15. https://doi.org/10.1186/s12896-020-00632-z
Huang, J., Huang, Z. L., Zhou, J. X., Li, C. Z., Yang, Z. H., Ruan, M., Li, H., Zhang, X., Wu, Z. J., Qin, X. L., Hu, J. H., Zhou, K. 2019. Enhancement of heavy metals removal by microbial flocculant produced by Paenibacillus polymyxa combined with an insufficient hydroxide precipitation. Chemical Engineer-ing Journal. 374:880–894. https://doi.org/10.1016/j.cej.2019.06.009
Hussein, M. H., Saeed, I. O. 2022. Phytoremedation: Plant Synergy - Bacteria for Treatment of Heavy Metals. Journal of Pharmaceutical Negative Results. 13(1):933–941. https://doi.org/10.47750/pnr.2022.13.S01.111
Irawati, W., Parhusip, A. J. N., Sopiah, N., Tnunay, J. A. 2016. The Role of Heavy Metals-Resistant Bac-teria Acinetobacter sp. in Copper Phytoremediation using Eichhornia crasippes [(Mart.) Solms]. Con-ference Proceedings: International Conference on Natural Resources and Life Sciences. 208–220. https://doi.org/10.18502/KLS.V3I5.995
Jan, U., Feiwen, R., Masood, J., Chun, S. C. 2020. Characterization of Soil Microorganism from Humus and Indigenous Microorganism Amendments. Mycobiology. 48(5):392–398. https://doi.org/10.1080/12298093.2020.1816154
Janda, J. M., Abbott, S. L. 2007. 16S rRNA gene sequencing for bacterial identification in the diagnostic laboratory: Pluses, perils, and pitfalls. Journal of Clinical Microbiology. 45(9):2761–2764. https://doi.org/10.1128/JCM.01228-07
Jiang, H. H., Cai, L. M., Wen, H. H., Hu, G. C., Chen, L. G., Luo, J. 2020. An integrated approach to quantifying ecological and human health risks from different sources of soil heavy metals. Science of the Total Environment. 1–41. https://doi.org/10.1016/j.scitotenv.2019.134466
Jiang, L., Jung, W. Y., Park, S. H., Kang, S. W., Lee, M. K., Lee, J. S., Lee, J. H., Lee, J. 2021. Draft Ge-nome Sequence of Peribacillus sp. AGMB 02131 isolated from feces of a Korean cow. Korean Jour-nal of Microbiology. 57(1):66–68. https://doi.org/10.7845/kjm.2021.0119
Johnson, J. S., Spakowicz, D. J., Hong, B. Y., Petersen, L. M., Demkowicz, P., Chen, L., Leopold, S. R., Hanson, B. M., Agresta, H. O., Gerstein, M., Sodergren, E., Weinstock, G. M. 2019. Evaluation of 16S rRNA gene sequencing for species and strain-level microbiome analysis. Nature Communications. 10(1):1–11. https://doi.org/10.1038/s41467-019-13036-1
Jung, J., Jeong, H., Kim, H. J., Lee, D. W., Lee, S. J. 2016. Complete genome sequence of Bacillus ocean-isediminis 2691, a reservoir of heavy-metal resistance genes. Marine Genomics. 30:1–4. https://doi.org/10.1016/j.margen.2016.07.002
Jung, J., Park, W. 2015. Acinetobacter species as model microorganisms in environmental microbiology: current state and perspectives. Applied Microbiology and Biotechnology. 99(6):2533–2548. https://doi.org/10.1007/s00253-015-6439-y
Kandasamy, S., Dananjeyan, B., Krishnamurthy, K., Benckiser, G. 2015. Aerobic cyanide degradation by bacterial isolates from cassava factory wastewater. Brazilian Journal of Microbiology. 46(3):659–666. https://doi.org/10.1590/S1517-838246320130516
Kapahi, M., Sachdeva, S. 2019. Bioremediation options for heavy metal pollution. Journal of Health and Pollution. 9(24):1–20. https://doi.org/10.5696/2156-9614-9.24.191203
Khamar, Z., Makhdoumi-Kakhki, A., Mahmudy Gharaie, M. H. 2015. Remediation of cyanide from the gold mine tailing pond by a novel bacterial co-culture. International Biodeterioration and Biodegrada-tion. 99:123–128. https://doi.org/10.1016/j.ibiod.2015.01.009
Kim, H. S., Srinivasan, S., Lee, S. S. 2015. Paenibacillus alba nov., Isolated from Peat Soil. Current Mi-crobiology. 70(6):865–870. https://doi.org/10.1007/s00284-015-0795-9
Kumar, B., and Gopal, D. 2015. Effective role of indigenous microorganisms for sustainable environment. 3 Biotech. 5:1–10. https://doi.org/10.1007/s13205-015-0293-6
Learman, D. R., Ahmad, Z., Brookshier, A., Henson, M. W., Hewitt, V., Lis, A., Morrison, C., Robinson, A., Todaro, E., Wologo, E., Wynne, S., Alm, E. W., Kourtev, P. S. 2019. Comparative genomics of 16 Microbacterium spp. that tolerate multiple heavy metals and antibiotics. PeerJ. 1–19. https://doi.org/10.7717/peerj.6258
Liu, P., Zhang, Y., Tang, Q., Shi, S. 2021. Bioremediation of metal-contaminated soils by microbial-ly-induced carbonate precipitation and its effects on ecotoxicity and long-term stability. Biochemical Engineering Journal. 166:1–27. https://doi.org/10.1016/j.bej.2020.107856
Mahjoubi, M., Jaouani, A., Guesmi, A., Ben Amor, S., Jouini, A., Cherif, H., Najjari, A., Boudabous, A., Koubaa, N., Cherif, A. 2013. Hydrocarbonoclastic bacteria isolated from petroleum contaminated sites In Tunisia: Isolation, identification and characterization of the biotechnological potential. New Bio-technology. 30(6):723–733. https://doi.org/10.1016/j.nbt.2013.03.004
Mathivanan, K., Chandirika, J. U., Vinothkanna, A., Yin, H., Liu, X., & Meng, D. 2021. Bacterial adaptive strategies to cope with metal toxicity in the contaminated environment – A review. Ecotoxicology and Environmental Safety, 226, 112863. https://doi.org/10.1016/J.ECOENV.2021.112863
Mekuto, L., Alegbeleye, O. O., Ntwampe, S. K. O., Ngongang, M. M., Mudumbi, J. B., Akinpelu, E. A. 2016. Co-metabolism of thiocyanate and free cyanide by Exiguobacterium acetylicum and Bacillus marisflavi under alkaline conditions. 3 Biotech. 6(173):1–11. https://doi.org/10.1007/s13205-016-0491-x
Méndez, V., Fuentes, S., Morgante, V., Hernández, M., González, M., Moore, E., Seeger, M. 2017. Novel hydrocarbonoclastic metal-tolerant Acinetobacter and pseudomonas strains from Aconcagua river oil-polluted soil. Journal of Soil Science and Plant Nutrition. 17(4):1074–1087. https://doi.org/10.4067/S0718-95162017000400017
Morrissey, E. M., Mau, R. L., Schwartz, E., Caporaso, J. G., DIjkstra, P., Van Gestel, N., Koch, B. J., Liu, C. M., Hayer, M., McHugh, T. A., Marks, J. C., Price, L. B., Hungate, B. A. 2016. Phylogenetic or-ganization of bacterial activity. The ISME Journal. 10(9):2336–2340. https://doi.org/10.1038/ismej.2016.28
Nagvenkar, G. S., & Ramaiah, N. (2010). Arsenite tolerance and biotransformation potential in estuarine bacteria. Ecotoxicology, 19(4), 604–613. https://doi.org/10.1007/S10646-009-0429-8/METRICS
Nutman, A., Lerner, A., Schwartz, D., Carmeli, Y. 2016. Evaluation of carriage and environmental con-tamination by carbapenem-resistant Acinetobacter baumannii. Clinical Microbiology and Infection. 1–12. https://doi.org/10.1016/j.cmi.2016.08.020
Ortega Sánchez, M. E., Morales, M. C., Morales, J. A., Osorio, G. P., Carlos, J., & Hernández, M. 2018. Bioedegradation of hydrocarbons by bacteria producing biosurfactants. Revista Latinoamericana El Ambiente y Las Ciencias, 9(21), 1643–1656. www.ncbi.nlm.nih.gov/blast/Blast.cgi
Onuoha, S. C. 2014. Stimulated Biodegradation of Spent Lubricating Motor Oil in Soil Amended with Animal Droppings. American Journal of BioScience. 2(1):19. https://doi.org/10.11648/j.ajbio.20140201.14
Pande, V., Pandey, S. C., Sati, D., Bhatt, P., & Samant, M. 2022. Microbial Interventions in Bioremedia-tion of Heavy Metal Contaminants in Agroecosystem. Frontiers in Microbiology, 13. https://doi.org/10.3389/FMICB.2022.824084
Patel, S., Gupta, R. S. 2020. A phylogenomic and comparative genomic framework for resolving the poly-phyly of the genus bacillus: Proposal for six new genera of bacillus species, Peribacillus gen. nov., Cytobacillus gen. nov., Mesobacillus gen. nov., Neobacillus gen. nov., Metabacillu. International Journal of Systematic and Evolutionary Microbiology. 70(1):406–438. https://doi.org/10.1099/ijsem.0.003775
Pereira, P. P., Torres Tejerizo, G. A., Fernandez, M., Blanch, A. R., Gonzalez, P. S., Agostini, E. 2020. Polyphasic characterization and identification of the bioremediation agent Bacillus sp. SFC 500-1E. Genomics. 112:4525–4535. https://doi.org/10.1016/j.ygeno.2020.08.008
Raina, V., Nayak, T., Ray, L., Kumari, K., Suar, M. 2019. A Polyphasic Taxonomic Approach for Desig-nation and Description of Novel Microbial Species. Microbial Diversity in the Genomic Era. 137–152. https://doi.org/10.1016/B978-0-12-814849-5.00009-5
Ran, X. Q., Hong, L., Tian, Q., Jiafu, W., You, L., Huang, S., Xi, N., Li, S. Mechanism of manganese oxi-dization of Bacillus safensis strain ST7 isolated from the soil of mineral area. [Consultado 13 de fe-brero 2023] 2020. ResearchGate. Disponible en: file:///D:/Documento/Descargas/Mechanism_of_manganese_oxidization_of_Bacillus_saf.pdf
Rawat, M., Rai, J. P. N. 2012. Adsorption of heavy metals by Paenibacillus validus strain MP5 isolated from industrial effluent-polluted soil. Bioremediation Journal. 16(2):66–73. https://doi.org/10.1080/10889868.2012.665959
Restrepo, O., Montoya, C., Muñoz, N. 2006. Microbial degradation of cyanide from gold metallurgical plants utilizing P.fluorecens. Dyna. 73(149):45–51. https://www.researchgate.net/publication/262467370
Rzymski, P., Klimaszyk, P., Marszelewski, W., Borowiak, D., Mleczek, M., Nowiński, K., Pius, B., Niedzielski, P., & Poniedziałek, B. 2017. The chemistry and toxicity of discharge waters from copper mine tailing impoundment in the valley of the Apuseni Mountains in Romania. Environmental Science and Pollution Research, 24(26), pp. 21445–21458. https://doi.org/10.1007/s11356-017-9782-y.
Salam, L. B., Obayori, O. S., Olatoye, N. O. 2014. Biodegradation of anthracene by a novel actinomycete, Microbacterium sp. isolated from tropical hydrocarbon-contaminated soil. World Journal of Microbi-ology and Biotechnology. 30(1):335–341. https://doi.org/10.1007/s11274-013-1437-7
Salam, M., Varma, A. 2019. Bacterial community structure in soils contaminated with electronic waste pol-lutants from Delhi NCR, India. Electronic Journal of Biotechnology. 41:72–80. https://doi.org/10.1016/j.ejbt.2019.07.003
Sermet, E. and Nieć, M. 2021. Not mining sterilization of explored mineral resources. The example of na-tive sulfur deposits in poland case history. Resources, 10(4), pp. 1–12. https://doi.org/10.3390/resources10040030.
Sernaque Aguilar, Y. A., Cornejo La Torre, M., Regard, J. P., Mialhe Matonnier, E. L. 2019. Caracterización molecular de bacterias cultivables y no cultivables procedentes de pozas de lixiviación con cianuro. Revista Peruana de Biología. 26(2):275–282. https://doi.org/10.15381/rpb.v26i2.16383
Sevak, P., Pushkar, B., & Mazumdar, S. 2023. Mechanistic evaluation of chromium bioremediation in Aci-netobacter junii strain b2w: A proteomic approach. Journal of Environmental Management, 328, 116978. https://doi.org/10.1016/J.JENVMAN.2022.116978
Sheng, X. F., Xia, J. J., Jiang, C. Y., He, L. Y., Qian, M. 2008. Characterization of heavy metal-resistant endophytic bacteria from rape (Brassica napus) roots and their potential in promoting the growth and lead accumulation of rape. Environmental Pollution. 156:1164–1170. https://doi.org/10.1016/j.envpol.2008.04.007
Shibulal, B., Al-Bahry, S. N., Al-Wahaibi, Y. M., Elshafie, A. E., Al-Bemani, A. S., Joshi, S. J. 2017. The potential of indigenous Paenibacillus ehimensis BS1 for recovering heavy crude oil by biotransfor-mation to light fractions. PLoS ONE. 12(2):1–18. https://doi.org/10.1371/journal.pone.0171432
Starostin, K. V., Demidov, E. A., Bryanskaya, A. V., Efimov, V. M., Rozanov, A. S., Peltek, S. E. 2015. Identification of Bacillus strains by MALDI TOF MS using geometric approach. Scientific Reports. 5:1–9. https://doi.org/10.1038/srep16989
Tarasov, K., Yakhnenko, A., Zarubin, M., Gangapshev, A., Potekhina, N. V., Avtukh, A. N., Kravchenko, E. 2023. Cytobacillus pseudoceanisediminis sp. nov., A Novel Facultative Methylotrophic Bacterium with High Heavy Metal Resistance Isolated from the Deep Underground Saline Spring. Current Mi-crobiology. 80(31):1–10. https://doi.org/10.1007/s00284-022-03141-8
Vaishnavi, S., Thamaraiselvi, C., Vasanthy, M. 2019. Efficiency of Indigenous Microorganisms in Biore-mediation of Tannery Effluent. Waste Water Recycling and Management. 151–168. https://doi.org/10.1007/978-981-13-2619-6_13
Valenzuela-González, F., Casillas-Hernández, R., Villalpando, E., Vargas-Albores, F. 2015. El Gen ARNr 16s en el estudio de comunidades microbianas marinas. Ciencias Marinas. 41(4):297–313. https://doi.org/10.7773/cm.v41i4.2492
Verma, S., Kuila, A. 2019. Bioremediation of heavy metals by microbial process. Environmental Technol-ogy and Innovation. 14(100369):1–11. https://doi.org/10.1016/j.eti.2019.100369
Woese, C. R. 1987. Bacterial evolution. Microbiological Reviews. 51(2):221–271. https://doi.org/10.1139/m88-093
Wuana, R. A., Okieimen, F. E. 2011. Heavy Metals in Contaminated Soils: A Review of Sources, Chemis-try, Risks and Best Available Strategies for Remediation. International Scholarly Research Network. 201:1–20. https://doi.org/10.5402/2011/402647
Wufuer, R., Li, W., Wang, S., Duo, J. 2022. Isolation and Degradation Characteristics of PBAT Film De-grading Bacteria. International Journal of Environmental Research and Public Health. 19(17087):1–12. https://doi.org/10.3390/ijerph192417087
Zahoor, A., Rehman, A. 2009. Isolation of Cr(VI) reducing bacteria from industrial effluents and their po-tential use in bioremediation of chromium containing wastewater. Journal of Environmental Sciences. 21(6):814–820. https://doi.org/10.1016/S1001-0742(08)62346-3
Zhang, H., Yuan, X., Xiong, T., Wang, H., Jiang, L. 2020. Bioremediation of co-contaminated soil with heavy metals and pesticides: Influence factors, mechanisms and evaluation methods. Chemical Engi-neering Journal. 398:1–19. https://doi.org/10.1016/j.cej.2020.125657
Zhou, Z., Charlesworth, J., Achtman, M. 2020. Accurate reconstruction of bacterial pan- and core genomes with PEPPAN. Genome Research. 30(11):1667–1679. https://doi.org/10.1101/gr.260828.120
Archivos adicionales
Publicado
Cómo citar
Número
Sección
Licencia
Derechos de autor 2023

Esta obra está bajo una licencia internacional Creative Commons Atribución-NoComercial-CompartirIgual 4.0.
La revista Biotecnia se encuentra bajo la licencia Atribución-NoComercial-CompartirIgual 4.0 Internacional (CC BY-NC-SA 4.0)









_(2).jpg)






